2026年 | プレスリリース・研究成果
遺伝子変異に合わせたRNA標的創薬へ RNA構造と低分子化合物の相互作用を大規模に検出する新技術 『BIVID-MaP』を開発
【本学研究者情報】
〇多元物質科学研究所 准教授 鬼塚和光
研究室ウェブサイト
【発表のポイント】
- RNA-低分子化合物相互作用の検出手法「BIVID-MaP」を開発しました
- 1塩基変異がRNA構造と結合能を変化させることを大規模に解明しました
- 個々の変異に最適化したRNA標的創薬と精密医療の実現への貢献が期待できます
【概要】
宮下映見 大学院生(京都大学iPS細胞研究所(CiRA)未来生命科学開拓部門・株式会社xFOREST Therapeutics)、小松リチャード馨 最高技術責任者(株式会社xFOREST Therapeutics)、齊藤博英 教授(CiRA未来生命科学開拓部門・東京大学定量生命科学研究所)、および鬼塚和光 准教授(東北大学多元物質科学研究所)らの研究グループは、遺伝子変異によって変化するRNA構造と低分子化合物の相互作用を大規模に検出する新技術「BIVID-MaP」を開発し、変異特異的な化合物結合を1塩基レベルの解像度で特定することに成功しました。
RNAの立体構造は、遺伝子発現を調節する重要な因子です。そのため、従来のタンパク質を標的とした手法ではアプローチが困難だった遺伝子を制御する、有望な創薬標的として注目されています。遺伝子の変異や個人間の遺伝的バリエーションはRNAの構造を変化させ、特定の低分子化合物に対する結合能(感受性)を左右することが知られています。しかし、これまで膨大な数の変異が低分子化合物との相互作用にどう影響するかを大規模に評価する手法は存在しませんでした。研究グループは、低分子化合物が標的RNAに結合した際に、そのRNA結合部位を化学修飾する「VQ(Vinyl-Quinazolinone)」ユニットと、逆転写注1反応時の塩基欠損を利用して結合部位を1塩基レベルの解像度で特定する「BIVID-MaP(Binding and VQ-induced Deletion-based Mutational Profiling)」法を構築しました(Fig. 1)。
この技術を用いて、代表的なRNA高次構造であるG4構造注2を対象に解析を行ったところ、G4構造の安定性や低分子化合物との結合状態を変化させる特定のがん変異の存在を明らかにしました。さらに、細胞溶解液という複雑な環境下においても、標的とするRNA構造への結合を正確に検出できることを実証しました。これらの成果は、個々の患者さんの遺伝的背景に基づいた「個別化医療」における、RNA標的創薬を加速させる強力なプラットフォームになることが期待されました。
この研究成果は2026年3月19日に「Nature Communications」で公開されます。
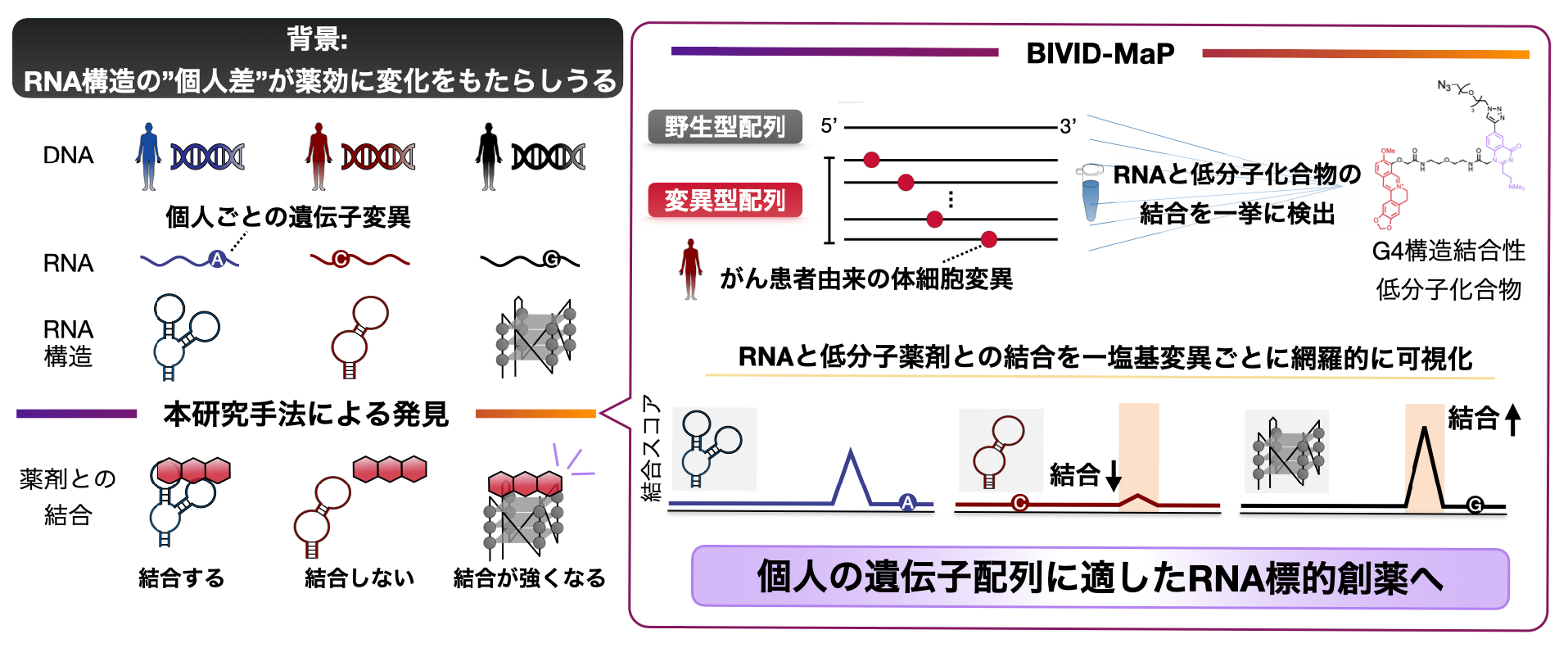
Fig. 1 本研究のまとめ
【用語解説】
注1) 逆転写
RNAを型としてDNA(cDNA)を合成する反応。本研究では、VQによる「印」がある場所でこの反応が止まったりスキップしたりする性質を利用し、化合物の結合場所を配列データ上の「欠損」として特定する。
注2) G4構造(G-quadruplex)
グアニン(G)が豊富なRNA配列が形作る、4本鎖の特殊な立体構造。病気の原因となる遺伝子の制御に深く関わっているため、創薬における有力なターゲットとなっている。
【論文情報】
論文名:"Systematic identification of variant-specific RNA structure-small molecule interactions exemplified by RNA G-quadruplexes"
ジャーナル名:Nature Communications
著者:Emi Miyashita1,2, Kazumitsu Onizuka3*, Yutong Chen3, Hiroki Yoshida2, Hina Hatayama3, Shunya Ishikawa3, Peijie Yan2, 4, Takahito Hasegawa3, Mamiko Ozawa3, Kaho Maeta2, Fumi Nagatsugi3, Hirohide Saito1,4*, Kaoru R. Komatsu2*
*責任著者
DOI:10.1038/s41467-026-70097-9
問い合わせ先
東北大学多元物質科学研究所
広報情報室
TEL: 022-217-5198
Email: press.tagen*grp.tohoku.ac.jp(*を@に置き換えてください)

![]()
東北大学は持続可能な開発目標(SDGs)を支援しています
